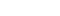단백질 서열 기반 ‘HIT-EC’…네이처 커뮤니케이션즈 게재
-

- ▲ 효소 기능 예측 AI 모델을 개발한 선문대 유전체 기반 BioIT 융합연구소 오태진(오른쪽) 교수와 한소라 교수.ⓒ선문대
선문대학교 유전체 기반 BioIT 융합연구소 오태진 교수 연구팀이 단백질 서열만으로 효소 기능을 예측할 수 있는 인공지능(AI) 모델을 개발해 국제 학술지에 발표했다.선문대는 오태진 교수와 한소라 교수가 미국 네바다대학교 라스베이거스(UNLV) 강민곤 교수, 극지연구소 이준혁 박사와 공동연구를 통해 효소 기능(EC 번호)을 예측하는 트랜스포머 기반 딥러닝 모델 ‘HIT-EC’를 개발했다고 밝혔다.효소는 생물체 내 화학 반응을 촉진하는 단백질로, 과학자들은 효소의 기능을 국제 표준 코드인 EC 번호(Enzyme Commission number)로 분류한다.EC 번호는 4단계 숫자로 구성된 계층형 분류 체계로, 단계가 깊어질수록 효소의 기능이 더욱 구체적으로 구분된다.연구팀이 개발한 ‘HIT-EC(Hierarchical Interpretable Transformer)’는 단백질 서열을 분석해 EC 번호를 예측하는 AI 모델이다.단순히 결과를 제시하는 데 그치지 않고, 단백질 서열 중 어떤 부분을 근거로 예측했는지 설명할 수 있는 ‘해석 가능성’을 갖춘 것이 특징이다.공동연구팀은 대규모 단백질 데이터셋과 다양한 평가 시나리오를 통해 모델 성능을 검증했다.그 결과 희귀 클래스와 서로 다른 종 환경에서도 안정적인 예측 성능과 높은 일반화 가능성을 확인했으며, 모델이 제시한 중요 서열 위치가 실제 촉매 모티프와 기능 잔기와도 일치하는 것으로 나타났다.오태진 교수는 “생명공학과 컴퓨터공학의 융합 연구를 통해 유전체 빅데이터를 신뢰 가능한 AI로 분석한 사례”라며 “효소 기능 예측의 정확도와 해석 가능성을 동시에 높여 디지털 헬스케어와 제약·바이오 산업 발전에 기여할 것으로 기대한다”고 말했다.한편 이번 연구는 ‘Trustworthy prediction of enzyme commission numbers using a hierarchical interpretable transformer’라는 제목으로 세계적 학술지 Nature Communications에 지난 1월 30일 게재됐으며, 한국을 빛낸 사람들(한빛사)에도 선정됐다.